Génome - Genome
| Fait partie d'une série sur |
| La génétique |
|---|
 |

Dans les domaines de la biologie moléculaire et de la génétique , un génome est l'ensemble des informations génétiques d'un organisme. Il est constitué de séquences nucléotidiques d' ADN (ou ARN dans les virus à ARN ). Le génome comprend à la fois les gènes (les régions codantes ) et l' ADN non codant , ainsi que l'ADN mitochondrial et l' ADN chloroplastique . L'étude du génome s'appelle la génomique . Le génome de plusieurs organismes a été séquencé et les gènes analysés, le projet du génome humain qui a séquencé l'intégralité du génome de l' Homo sapiens s'est achevé avec succès en avril 2003 .
Origine du terme
Le terme génome a été créé en 1920 par Hans Winkler , professeur de botanique à l' université de Hambourg , en Allemagne. Le dictionnaire Oxford suggère que le nom est un mélange des mots gène et chromosome . Cependant, voir omics pour une discussion plus approfondie. Quelques mots -ome apparentés existaient déjà, tels que biome et rhizome , formant un vocabulaire dans lequel s'insère systématiquement le génome .
Séquençage et cartographie
Une séquence génomique est la liste complète des nucléotides (A, C, G et T pour les génomes à ADN) qui composent tous les chromosomes d'un individu ou d'une espèce. Au sein d'une espèce, la grande majorité des nucléotides sont identiques entre les individus, mais le séquençage de plusieurs individus est nécessaire pour comprendre la diversité génétique.
En 1976, Walter Fiers de l' Université de Gand (Belgique) a été le premier à établir la séquence nucléotidique complète d'un génome à ARN viral ( Bacteriophage MS2 ). L'année suivante, Fred Sanger a terminé la première séquence ADN-génome : Phage Φ-X174 , de 5386 paires de bases. Les premières séquences du génome complet entre les trois domaines de la vie ont été libérés dans une courte période au milieu des années 1990: Le premier génome bactérien à séquencer était celle de Haemophilus influenzae , complétée par une équipe de l'Institut pour la recherche génomique en 1995. A Quelques mois plus tard, le premier génome eucaryote était achevé, avec les séquences des 16 chromosomes de la levure bourgeonnante Saccharomyces cerevisiae publiées à la suite d'un effort mené par l'Europe et commencé au milieu des années 1980. La première séquence du génome d'un archéon , Methanococcus jannaschii , a été achevée en 1996, encore une fois par l'Institute for Genomic Research.
Le développement de nouvelles technologies a rendu le séquençage du génome considérablement moins cher et plus facile, et le nombre de séquences complètes du génome augmente rapidement. Les National Institutes of Health des États-Unis conservent l'une des nombreuses bases de données complètes d'informations génomiques. Parmi les milliers de projets de séquençage du génome achevés figurent ceux du riz , d'une souris , de la plante Arabidopsis thaliana , du poisson-globe et de la bactérie E. coli . En décembre 2013, des scientifiques ont pour la première fois séquencé l'intégralité du génome d'un Néandertal , une espèce humaine éteinte . Le génome a été extrait de l' os de l' orteil d'un Néandertalien de 130 000 ans trouvé dans une grotte sibérienne .
Les nouvelles technologies de séquençage, telles que le séquençage parallèle massif, ont également ouvert la perspective du séquençage du génome personnel en tant qu'outil de diagnostic, comme l'a lancé Manteia Predictive Medicine . Une étape majeure vers cet objectif a été l'achèvement en 2007 du génome complet de James D. Watson , l'un des co-découvreurs de la structure de l'ADN.
Alors qu'une séquence de génome répertorie l'ordre de chaque base d'ADN dans un génome, une carte du génome identifie les points de repère. Une carte du génome est moins détaillée qu'une séquence du génome et facilite la navigation dans le génome. Le Human Genome Project a été organisé pour cartographier et séquencer le génome humain . Une étape fondamentale du projet a été la publication d'une carte génomique détaillée par Jean Weissenbach et son équipe au Genoscope à Paris.
Les séquences et les cartes du génome de référence continuent d'être mises à jour, supprimant les erreurs et clarifiant les régions à haute complexité allélique. Le coût décroissant de la cartographie génomique a permis aux sites généalogiques de l'offrir en tant que service, dans la mesure où l'on peut soumettre son génome à des efforts scientifiques de crowdsourcing tels que DNA.LAND au New York Genome Center , un exemple à la fois des économies d'échelle et de la science citoyenne .
Génomes viraux
Les génomes viraux peuvent être composés d'ARN ou d'ADN. Les génomes de virus à ARN peuvent être soit un ARN simple brin ou d' ARN double brin , et peuvent contenir une ou plusieurs molécules d'ARN séparées (segments: monopartit ou génome multipartit). Les virus à ADN peuvent avoir des génomes simple brin ou double brin. La plupart des génomes de virus à ADN sont composés d'une seule molécule linéaire d'ADN, mais certains sont constitués d'une molécule d'ADN circulaire. Il existe également des ARN viraux appelés ARN simple brin : sert de matrice pour la synthèse d'ARNm et ARN simple brin : sert de matrice pour la synthèse d'ADN.
L'enveloppe virale est une couche externe de membrane que les génomes viraux utilisent pour entrer dans la cellule hôte. Certaines des classes d'ADN et d'ARN viraux sont constituées d'une enveloppe virale, d'autres non.
Génomes procaryotes
Les procaryotes et les eucaryotes ont des génomes à ADN. Les archées et la plupart des bactéries ont un seul chromosome circulaire , cependant, certaines espèces bactériennes ont des chromosomes linéaires ou multiples. Si l'ADN est répliqué plus rapidement que les cellules bactériennes ne se divisent, plusieurs copies du chromosome peuvent être présentes dans une seule cellule, et si les cellules se divisent plus rapidement que l'ADN ne peut être répliqué, la réplication multiple du chromosome est initiée avant que la division ne se produise, permettant aux cellules filles d'hériter de génomes complets et de chromosomes déjà partiellement répliqués. La plupart des procaryotes ont très peu d'ADN répétitif dans leur génome. Cependant, certaines bactéries symbiotiques (par exemple Serratia symbiotica ) ont des génomes réduits et une fraction élevée de pseudogènes : seulement ~ 40 % de leur ADN code pour des protéines.
Certaines bactéries possèdent du matériel génétique auxiliaire, faisant également partie de leur génome, qui est porté par des plasmides . Pour cela, le mot génome ne doit pas être utilisé comme synonyme de chromosome .
Génomes eucaryotes
Les génomes eucaryotes sont composés d'un ou plusieurs chromosomes d'ADN linéaires. Le nombre de chromosomes varie considérablement d'une fourmi sauteuse Jack et d'un némotode asexué , qui n'ont chacun qu'une paire, à une espèce de fougère qui en compte 720 paires. Il est surprenant de constater la quantité d'ADN que contiennent les génomes eucaryotes par rapport aux autres génomes. La quantité est encore plus que ce qui est nécessaire pour les gènes codant et non codant pour les protéines d'ADN en raison du fait que les génomes eucaryotes présentent une variation de 64 000 fois dans leurs tailles. Cependant, cette particularité est due à la présence d'ADN répétitif et d'éléments transposables (ET).
Une cellule humaine typique a deux copies de chacun des 22 autosomes , un hérité de chaque parent, plus deux chromosomes sexuels , ce qui la rend diploïde. Les gamètes , tels que les ovules, les spermatozoïdes, les spores et le pollen, sont haploïdes, ce qui signifie qu'ils ne portent qu'une seule copie de chaque chromosome. En plus des chromosomes du noyau, les organites tels que les chloroplastes et les mitochondries ont leur propre ADN. On dit parfois que les mitochondries ont leur propre génome, souvent appelé « génome mitochondrial ». L'ADN trouvé dans le chloroplaste peut être appelé « plastome ». Comme les bactéries dont ils sont issus, les mitochondries et les chloroplastes ont un chromosome circulaire.
Contrairement aux procaryotes, les eucaryotes ont une organisation exon-intron des gènes codant pour les protéines et des quantités variables d'ADN répétitif. Chez les mammifères et les plantes, la majorité du génome est composée d'ADN répétitif. Les gènes des génomes eucaryotes peuvent être annotés à l'aide de FINDER.
Séquences de codage
Les séquences d'ADN qui portent les instructions pour fabriquer des protéines sont appelées séquences codantes. La proportion du génome occupée par des séquences codantes varie considérablement. Un génome plus grand ne contient pas nécessairement plus de gènes, et la proportion d'ADN non répétitif diminue avec l'augmentation de la taille du génome chez les eucaryotes complexes.
Séquences non codantes
Les séquences non codantes comprennent les introns , les séquences pour les ARN non codants, les régions régulatrices et l'ADN répétitif. Les séquences non codantes représentent 98% du génome humain. Il existe deux catégories d'ADN répétitif dans le génome : les répétitions en tandem et les répétitions intercalées.
Répétitions en tandem
Les séquences courtes non codantes qui sont répétées tête-bêche sont appelées répétitions en tandem . Les microsatellites se composent de 2 à 5 répétitions de paires de bases, tandis que les répétitions de minisatellites sont de 30 à 35 pb. Les répétitions en tandem représentent environ 4 % du génome humain et 9 % du génome de la mouche des fruits. Les répétitions en tandem peuvent être fonctionnelles. Par exemple, les télomères sont composés de la répétition en tandem TTAGGG chez les mammifères, et ils jouent un rôle important dans la protection des extrémités du chromosome.
Dans d'autres cas, l'augmentation du nombre de répétitions en tandem dans les exons ou les introns peut provoquer une maladie . Par exemple, le gène humain huntingtine contient généralement 6 à 29 répétitions en tandem des nucléotides CAG (codant pour un tractus polyglutamine). Une expansion à plus de 36 répétitions entraîne la maladie de Huntington , une maladie neurodégénérative. Vingt troubles humains sont connus pour résulter d'expansions répétées en tandem similaires dans divers gènes. Le mécanisme par lequel les protéines à faisceaux expansés de polygulatamine provoquent la mort des neurones n'est pas entièrement compris. Une possibilité est que les protéines ne se replient pas correctement et évitent la dégradation, au lieu de s'accumuler en agrégats qui séquestrent également des facteurs de transcription importants, modifiant ainsi l'expression des gènes.
Les répétitions en tandem sont généralement causées par un glissement pendant la réplication, un croisement inégal et une conversion génique.
Éléments transposables
Les éléments transposables (TE) sont des séquences d'ADN avec une structure définie qui sont capables de changer leur emplacement dans le génome. Les ET sont classés soit comme un mécanisme qui se réplique par copier-coller, soit comme un mécanisme qui peut être excisé du génome et inséré à un nouvel emplacement. Dans le génome humain, il existe trois classes importantes d'ET qui constituent plus de 45 % de l'ADN humain ; ces classes sont les éléments nucléaires longs intercalés (LINE), les éléments nucléaires intercalés (SINE) et les rétrovirus endogènes. Ces éléments ont un grand potentiel pour modifier le contrôle génétique dans un organisme hôte.
Le mouvement des TE est une force motrice de l'évolution du génome chez les eucaryotes car leur insertion peut perturber les fonctions des gènes, la recombinaison homologue entre les TE peut produire des duplications et les TE peuvent déplacer les exons et les séquences régulatrices vers de nouveaux emplacements.
Rétrotransposons
Les rétrotransposons se trouvent principalement chez les eucaryotes mais ne se trouvent pas chez les procaryotes et les rétrotransposons forment une grande partie des génomes de nombreux eucaryotes. Le rétrotransposon est un élément transposable qui se transpose via un ARN intermédiaire. Les rétrotransposons sont composés d' ADN , mais sont transcrits en ARN pour la transposition, puis le transcrit d'ARN est recopié dans la formation d'ADN à l'aide d'une enzyme spécifique appelée transcriptase inverse. Les rétrotransposons qui portent la transcriptase inverse dans leur gène peuvent déclencher sa propre transposition mais les gènes dépourvus de la transcriptase inverse doivent utiliser la transcriptase inverse synthétisée par un autre rétrotransposon. Les rétrotransposons peuvent être transcrits en ARN, qui sont ensuite dupliqués à un autre site dans le génome. Les rétrotransposons peuvent être divisés en répétitions terminales longues (LTR) et en répétitions terminales non longues (Non-LTR).
Les longues répétitions terminales (LTR) sont dérivées d'infections rétrovirales anciennes, elles codent donc pour des protéines liées aux protéines rétrovirales, notamment gag (protéines structurelles du virus), pol (transcriptase inverse et intégrase), pro (protéase) et, dans certains cas, env ( enveloppe) gènes. Ces gènes sont flanqués de longues répétitions aux extrémités 5' et 3'. Il a été rapporté que les LTR constituent la plus grande fraction du génome de la plupart des plantes et pourraient expliquer l'énorme variation de la taille du génome.
Les répétitions terminales non longues (Non-LTR) sont classées en éléments nucléaires intercalés longs (LINE), éléments nucléaires intercalés courts (SINE) et éléments de type Penelope (PLE). Dans Dictyostelium discoideum , il existe un autre élément de type DIRS appartenant aux non-LTR. Les non-LTR sont largement répandus dans les génomes eucaryotes.
Les éléments longs intercalés (LINE) codent pour les gènes de la transcriptase inverse et de l'endonucléase, ce qui en fait des éléments transposables autonomes. Le génome humain compte environ 500 000 LIGNES, représentant environ 17 % du génome.
Les éléments courts intercalés (SINE) ont généralement moins de 500 paires de bases et ne sont pas autonomes, ils dépendent donc des protéines codées par les LINE pour la transposition. L' élément Alu est le SINE le plus courant chez les primates. Il compte environ 350 paires de bases et occupe environ 11% du génome humain avec environ 1 500 000 copies.
transposons d'ADN
Les transposons d'ADN codent pour une enzyme transposase entre les répétitions terminales inversées. Lorsqu'elle est exprimée, la transposase reconnaît les répétitions inversées terminales qui flanquent le transposon et catalyse son excision et sa réinsertion dans un nouveau site. Ce mécanisme de copier-coller réinsère généralement les transposons à proximité de leur emplacement d'origine (à moins de 100 Ko). Les transposons d'ADN se trouvent dans les bactéries et représentent 3 % du génome humain et 12 % du génome du ver rond C. elegans .
Taille du génome
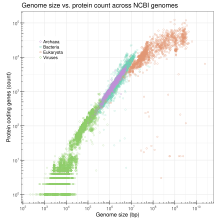
La taille du génome est le nombre total de paires de bases d'ADN dans une copie d'un génome haploïde . La taille du génome varie considérablement d'une espèce à l'autre. Les invertébrés ont de petits génomes, ceci est également corrélé à un petit nombre d'éléments transposables. Les poissons et les amphibiens ont des génomes de taille intermédiaire et les oiseaux ont des génomes relativement petits, mais il a été suggéré que les oiseaux ont perdu une partie substantielle de leur génome pendant la phase de transition vers le vol. Avant cette perte, la méthylation de l'ADN permet l'expansion adéquate du génome.
Chez l'homme, le génome nucléaire comprend environ 3,2 milliards de nucléotides d'ADN, divisés en 24 molécules linéaires, les plus courtes de 50 000 000 de nucléotides et les plus longues de 260 000 000 de nucléotides, chacune contenue dans un chromosome différent. Il n'y a pas de corrélation claire et cohérente entre la complexité morphologique et la taille du génome chez les procaryotes ou les eucaryotes inférieurs . La taille du génome est en grande partie fonction de l'expansion et de la contraction des éléments répétitifs de l'ADN.
Les génomes étant très complexes, une stratégie de recherche consiste à réduire au strict minimum le nombre de gènes dans un génome tout en permettant à l'organisme en question de survivre. Des travaux expérimentaux sont en cours sur les génomes minimaux pour les organismes unicellulaires ainsi que sur les génomes minimaux pour les organismes multicellulaires (voir Biologie du développement ). Le travail est à la fois in vivo et in silico .
Taille du génome due aux éléments transposables
Il existe de nombreuses différences énormes de taille dans les génomes, spécialement mentionnées auparavant dans les génomes eucaryotes multicellulaires. La principale raison pour laquelle il existe une si grande variété de tailles est due à la présence d'éléments transposables. Les ET sont connus pour contribuer à un changement significatif dans la masse d'ADN d'une cellule. Ce processus est corrélé à leur hébergement à long terme dans le génome hôte, et donc, à l'expansion de la taille du génome.
Voici un tableau de quelques génomes significatifs ou représentatifs. Voir #Voir aussi pour les listes de génomes séquencés.
| Type d'organisme | Organisme | Taille du génome ( paires de bases ) |
Environ. non. des gènes | Noter | |
|---|---|---|---|---|---|
| Virus | Circovirus porcin de type 1 | 1 759 | 1,8 Ko | Les plus petits virus se répliquent de manière autonome dans les cellules eucaryotes . | |
| Virus | Bactériophage MS2 | 3 569 | 3,5 Ko | Premier génome à ARN séquencé | |
| Virus | SV40 | 5 224 | 5,2 Ko | ||
| Virus | Phage Φ-X174 | 5 386 | 5,4 Ko | Premier ADN-génome séquencé | |
| Virus | VIH | 9 749 | 9,7 Ko | ||
| Virus | Phage | 48 502 | 48,5 Ko | Souvent utilisé comme vecteur pour le clonage d'ADN recombinant.
|
|
| Virus | Mégavirus | 1 259 197 | 1,3 Mo | Jusqu'en 2013, le plus grand génome viral connu. | |
| Virus | Pandorevirus salinus | 2 470 000 | 2,47 Mo | Le plus grand génome viral connu. | |
| organite eucaryote | Mitochondrie humaine | 16 569 | 16,6 Ko | ||
| Bactérie | Nasuia deltocephalinicola (souche NAS-ALF) | 112 091 | 112 Ko | 137 | Le plus petit génome non viral connu. Symbiote des cicadelles . |
| Bactérie | Carsonella ruddii | 159.662 | 160 Ko | Un endosymbiote des insectes psylles | |
| Bactérie | Buchnera aphidicola | 600 000 | 600 Ko | Un endosymbiote de pucerons | |
| Bactérie | Wigglesworthia glossinidia | 700 000 | 700 Ko | Un symbiote dans l'intestin de la mouche tsé-tsé | |
| Bactérie – cyanobactérie | Prochlorococcus spp. (1,7 Mo) | 1 700 000 | 1,7 Mo | 1 884 | Le plus petit génome de cyanobactérie connu. L'un des principaux photosynthétiseurs sur Terre. |
| Bactérie | Haemophilus influenzae | 1.830.000 | 1,8 Mo | Premier génome d'un organisme vivant séquencé, juillet 1995 | |
| Bactérie | Escherichia coli | 4 600 000 | 4,6 Mo | 4 288 | |
| Bactérie – cyanobactérie | Nostoc punctiforme | 9 000 000 | 9 Mo | 7 432 | 7432 cadres de lecture ouverts |
| Bactérie | Solibacter usitatus (souche Ellin 6076) | 9 970 000 | 10 Mo | ||
| amiboïde | Polychaos dubium ( " Amoeba " dubia ) | 670 000 000 000 | 670 Go | Le plus grand génome connu. (Contesté) | |
| Plante | Genlisea tuberosa | 61 000 000 | 61 Mo | Plus petit génome de plante à fleurs enregistré , 2014. | |
| Plante | Arabidopsis thaliana | 135 000 000 | 135 Mo | 27 655 | Premier séquençage du génome végétal, décembre 2000. |
| Plante | Populus trichocarpa | 480 000 000 | 480 Mo | 73 013 | Premier génome d'arbre séquencé, septembre 2006 |
| Plante | Fritillaria assyriaca | 130 000 000 000 | 130 Go | ||
| Plante | Paris japonica (natif du Japon, pâle-pétale) | 150 000 000 000 | 150 Go | Le plus grand génome végétal connu | |
| Plante – mousse | Physcomitrella patens | 480 000 000 | 480 Mo | Premier génome d'une bryophyte séquencé, janvier 2008. | |
| Champignon – levure | Saccharomyces cerevisiae | 12 100 000 | 12,1 Mo | 6 294 | Premier séquençage du génome eucaryote, 1996 |
| Champignon | Aspergillus nidulans | 30 000 000 | 30 Mo | 9 541 | |
| Nématode | Pratylenchus coffeae | 20 000 000 | 20 Mo | Le plus petit génome animal connu | |
| Nématode | Caenorhabditis elegans | 100 300 000 | 100 Mo | 19 000 | Premier séquençage du génome animal multicellulaire, décembre 1998 |
| Insecte | Drosophila melanogaster (mouche des fruits) | 175 000 000 | 175 Mo | 13.600 | Variation de taille basée sur la souche (175-180Mb ; la souche yw standard est de 175Mb) |
| Insecte | Apis mellifera (abeille domestique) | 236 000 000 | 236 Mo | 10 157 | |
| Insecte | Bombyx mori (mite à soie) | 432.000.000 | 432 Mo | 14 623 | 14 623 gènes prédits |
| Insecte | Solenopsis invicta (fourmi de feu) | 480 000 000 | 480 Mo | 16 569 | |
| Mammifère | Mus musculus | 2 700 000 000 | 2,7 Go | 20 210 | |
| Mammifère | Pan paniscus | 3 286 640 000 | 3,3 Go | 20 000 | Bonobo - taille du génome estimée à 3,29 milliards de pb |
| Mammifère | Homo sapiens | 3 000 000 000 | 3 Go | 20 000 |
Taille du génome d' Homo sapiens estimée à 3,2 Gbp en 2001
Séquençage initial et analyse du génome humain |
| Oiseau | Gallus gallus | 1 043 000 000 | 1,0 Go | 20 000 | |
| Poisson | Tetraodon nigroviridis (type de poisson-globe) | 385 000 000 | 390 Mo | Le plus petit génome de vertébré connu est estimé à 340 Mb – 385 Mb. | |
| Poisson | Protopterus aethiopicus (poisson-poumon marbré) | 130 000 000 000 | 130 Go | Le plus grand génome de vertébré connu | |
Altérations génomiques
Toutes les cellules d'un organisme proviennent d'une seule cellule, on s'attend donc à ce qu'elles aient des génomes identiques ; cependant, dans certains cas, des différences apparaissent. Le processus de copie de l'ADN pendant la division cellulaire et l'exposition à des agents mutagènes environnementaux peuvent entraîner des mutations dans les cellules somatiques. Dans certains cas, de telles mutations conduisent au cancer car elles entraînent une division plus rapide des cellules et envahissent les tissus environnants. Dans certains lymphocytes du système immunitaire humain, la recombinaison V(D)J génère différentes séquences génomiques telles que chaque cellule produit un anticorps unique ou des récepteurs de cellules T.
Au cours de la méiose , les cellules diploïdes se divisent deux fois pour produire des cellules germinales haploïdes. Au cours de ce processus, la recombinaison entraîne un remaniement du matériel génétique à partir de chromosomes homologues, de sorte que chaque gamète possède un génome unique.
Reprogrammation à l'échelle du génome
La reprogrammation à l'échelle du génome dans les cellules germinales primordiales de souris implique l' effacement de l'empreinte épigénétique conduisant à la totipotence . La reprogrammation est facilitée par la déméthylation active de l' ADN , un processus qui implique la voie de réparation par excision des bases de l'ADN . Cette voie est utilisée dans l'effacement de la méthylation CpG (5mC) dans les cellules germinales primordiales. L'effacement de 5mC se produit via sa conversion en 5-hydroxyméthylcytosine (5hmC) entraînée par des niveaux élevés des enzymes dioxygénase dix-onze TET1 et TET2 .
Évolution du génome
Les génomes sont plus que la somme des gènes d'un organisme et ont des traits qui peuvent être mesurés et étudiés sans référence aux détails de gènes particuliers et de leurs produits. Les chercheurs comparent des traits tels que le caryotype (nombre de chromosomes), la taille du génome , l'ordre des gènes, le biais d'utilisation des codons et le contenu en GC pour déterminer quels mécanismes auraient pu produire la grande variété de génomes qui existent aujourd'hui (pour des aperçus récents, voir Brown 2002 ; Saccone et Pesole 2003 ; Benfey et Protopapas 2004 ; Gibson et Muse 2004 ; Reese 2004 ; Gregory 2005).
Les duplications jouent un rôle majeur dans la formation du génome. La duplication peut aller de l'extension de courtes répétitions en tandem à la duplication d'un groupe de gènes et jusqu'à la duplication de chromosomes entiers ou même de génomes entiers . De telles duplications sont probablement fondamentales pour la création de la nouveauté génétique.
Le transfert horizontal de gènes est invoqué pour expliquer comment il existe souvent une similitude extrême entre de petites portions des génomes de deux organismes qui sont par ailleurs très éloignés. Le transfert horizontal de gènes semble être courant chez de nombreux microbes . De plus, les cellules eucaryotes semblent avoir subi un transfert de matériel génétique de leurs génomes chloroplastiques et mitochondriaux vers leurs chromosomes nucléaires. Des données empiriques récentes suggèrent un rôle important des virus et des réseaux d'ARN sous-viraux pour représenter un rôle moteur principal pour générer une nouveauté génétique et une édition naturelle du génome.
Dans la fiction
Les travaux de science-fiction illustrent les préoccupations concernant la disponibilité des séquences du génome.
Le roman Jurassic Park de 1990 de Michael Crichton et le film suivant racontent l'histoire d'un milliardaire qui crée un parc à thème de dinosaures clonés sur une île éloignée, avec des résultats désastreux. Un généticien extrait l'ADN de dinosaure du sang d'anciens moustiques et comble les lacunes avec l'ADN d'espèces modernes pour créer plusieurs espèces de dinosaures. Un théoricien du chaos est invité à donner son avis d'expert sur la sécurité de l'ingénierie d'un écosystème avec les dinosaures, et il avertit à plusieurs reprises que les résultats du projet seront imprévisibles et finalement incontrôlables. Ces avertissements sur les dangers de l'utilisation de l'information génomique sont un thème majeur du livre.
Le film de 1997 Gattaca se déroule dans une société futuriste où les génomes des enfants sont conçus pour contenir la combinaison la plus idéale des traits de leurs parents, et des mesures telles que le risque de maladie cardiaque et l'espérance de vie prévue sont documentées pour chaque personne en fonction de leur génome. Les personnes conçues en dehors du programme eugéniste, connues sous le nom de « In-Valids », subissent des discriminations et sont reléguées à des occupations subalternes. Le protagoniste du film est un In-Valid qui travaille pour défier les prétendues probabilités génétiques et réaliser son rêve de travailler comme navigateur spatial. Le film met en garde contre un avenir où l'information génomique alimente les préjugés et les différences de classe extrêmes entre ceux qui peuvent et ne peuvent pas se permettre des enfants génétiquement modifiés.
Voir également
- Taille du génome bactérien
- Cryoconservation des ressources zoogénétiques
- Navigateur de génome
- Compilateur de génome
- Topologie du génome
- Étude d'association à l'échelle du génome
- Liste des génomes animaux séquencés
- Liste des génomes d'archées séquencés
- Liste des génomes bactériens séquencés
- Liste des génomes eucaryotes séquencés
- Liste des génomes de champignons séquencés
- Liste des génomes végétaux séquencés
- Liste des plastomes séquencés
- Liste des génomes de protistes séquencés
- Métagénomique
- Microbiome
- Épidémiologie moléculaire
- Épidémiologie pathologique moléculaire
- Pathologie moléculaire
- Séquence d'acide nucléique
- Pan-génome
- Médecine de précision
- Gène régulateur
- Séquençage du génome entier
Les références
Lectures complémentaires
- Benfey P, Protopapas AD (2004). L'essentiel de la génomique . Prentice Hall.
- Brown TA (2002). Génomes 2 . Oxford : Bios Scientific Publishers. ISBN 978-1-85996-029-5.
- Gibson G, Muse SV (2004). A Primer of Genome Science (Deuxième éd.). Sunderland, Masse : Sinauer Assoc. ISBN 978-0-87893-234-4.
- Grégory TR (2005). L'évolution du génome . Elsevier. ISBN 978-0-12-301463-4.
- Reece RJ (2004). Analyse des gènes et des génomes . Chichester : John Wiley & Fils. ISBN 978-0-470-84379-6.
- Saccone C, Pesole G (2003). Manuel de génomique comparée . Chichester : John Wiley & Fils. ISBN 978-0-471-39128-9.
- Werner E (décembre 2003). « Biologie des systèmes multicellulaires in silico et génomes minimaux ». Découverte de médicaments aujourd'hui . 8 (24) : 1121–27. doi : 10.1016/S1359-6446(03)02918-0 . PMID 14678738 .
Liens externes
- UCSC Genome Browser - affichez le génome et les annotations de plus de 80 organismes.
- genomecenter.howard.edu
- Construire une molécule d'ADN
- Quelques tailles de génomes comparatives
- DNA Interactive : L'histoire de la science de l'ADN
- L'ADN depuis le début
- Tout sur le projet du génome humain — de Genome.gov
- Base de données sur la taille du génome animal
- Base de données sur la taille du génome végétal
- OR : Base de données Genomes OnLine
- Le réseau d'information sur le génome
- Base de données du projet NCBI Entrez Genome
- Amorce du génome NCBI
- GeneCards — une base de données intégrée de gènes humains
- BBC News – Publication du dernier « chapitre » du génome
- IMG (The Integrated Microbial Genomes system)—pour l'analyse du génome par le DOE-JGI
- Analyse de données de séquençage de nouvelle génération de GeKnome Technologies — Analyse de données de séquençage de nouvelle génération pour Illumina et 454 Service de GeKnome Technologies.