Dihydrofolate réductase - Dihydrofolate reductase
| Dihydrofolate réductase | |||||||||
|---|---|---|---|---|---|---|---|---|---|
 Structure cristalline de la dihydrofolate réductase de foie de poulet. Entrée PDB 8dfr
| |||||||||
| Identifiants | |||||||||
| CE n° | 1.5.1.3 | ||||||||
| N ° CAS. | 9002-03-3 | ||||||||
| Bases de données | |||||||||
| IntEnz | Vue IntEnz | ||||||||
| BRENDA | Entrée BRENDA | ||||||||
| ExPASy | Vue NiceZyme | ||||||||
| KEGG | Entrée KEGG | ||||||||
| MétaCycle | voie métabolique | ||||||||
| PRIAM | profil | ||||||||
| Structures de l' APB | RCSB PDB PDBe PDBsum | ||||||||
| Ontologie des gènes | AmiGO / QuickGO | ||||||||
| |||||||||
| Dihydrofolate réductase | |||||||||
|---|---|---|---|---|---|---|---|---|---|
| Identifiants | |||||||||
| symbole | DHFR_1 | ||||||||
| Pfam | PF00186 | ||||||||
| Clan Pfam | CL0387 | ||||||||
| InterPro | IPR001796 | ||||||||
| PROSITE | PDOC00072 | ||||||||
| SCOP2 | 1dhi / SCOPe / SUPFAM | ||||||||
| |||||||||
| R67 dihydrofolate réductase | |||||||||
|---|---|---|---|---|---|---|---|---|---|
 Structure à haute résolution d'une dihydrofolate réductase codée par un plasmide de E. coli . Entrée PDB 2gqv
| |||||||||
| Identifiants | |||||||||
| symbole | DHFR_2 | ||||||||
| Pfam | PF06442 | ||||||||
| InterPro | IPR009159 | ||||||||
| SCOP2 | 1vif / SCOPe / SUPFAM | ||||||||
| |||||||||
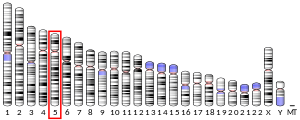
La dihydrofolate reductase , ou DHFR , est une enzyme qui réduit l' acide dihydrofolique de l' acide tétrahydrofolique , en utilisant NADPH en tant que donneur d'électrons , qui peut être converti en les types de tétrahydrofolate cofacteurs utilisés dans la chimie de transfert 1-carbone. Chez l'homme, l'enzyme DHFR est codée par le gène DHFR . On le trouve dans la région q11→q22 du chromosome 5. Les espèces bactériennes possèdent des enzymes DHFR distinctes (basées sur leur schéma de liaison des molécules diaminohétérocycliques), mais les DHFR des mammifères sont très similaires.
Structure
Une feuille centrale plissée bêta à huit brins constitue la principale caractéristique du repliement du squelette polypeptidique de la DHFR. Sept de ces brins sont parallèles et le huitième est antiparallèle. Quatre hélices alpha relient des brins bêta successifs. Les résidus 9 à 24 sont appelés « Met20 » ou « boucle 1 » et, avec d'autres boucles, font partie du sous-domaine principal qui entoure le site actif . Le site actif est situé dans la moitié N-terminale de la séquence, qui comprend un dipeptide Pro - Trp conservé ; il a été démontré que le tryptophane est impliqué dans la liaison du substrat par l'enzyme.
Fonction
La dihydrofolate réductase convertit le dihydrofolate en tétrahydrofolate , une navette protonique nécessaire à la synthèse de novo des purines , de l' acide thymidylique et de certains acides aminés . Alors que le gène fonctionnel de la dihydrofolate réductase a été cartographié sur le chromosome 5, plusieurs pseudogènes traités sans intron ou des gènes de type dihydrofolate réductase ont été identifiés sur des chromosomes séparés.
Présent dans tous les organismes, le DHFR joue un rôle essentiel dans la régulation de la quantité de tétrahydrofolate dans la cellule. Le tétrahydrofolate et ses dérivés sont essentiels à la synthèse des purines et des thymidylates , qui sont importants pour la prolifération et la croissance cellulaires. La DHFR joue un rôle central dans la synthèse des précurseurs d' acides nucléiques , et il a été démontré que les cellules mutantes qui manquent complètement de DHFR ont besoin de glycine, d'un acide aminé et de thymidine pour se développer. La DHFR a également été démontrée comme une enzyme impliquée dans la récupération de la tétrahydrobioptérine à partir de la dihydrobioptérine
Mécanisme
Mécanisme général
DHFR catalyse le transfert d'un hydrure de NADPH au dihydrofolate avec une protonation d'accompagnement pour produire du tétrahydrofolate . À la fin, le dihydrofolate est réduit en tétrahydrofolate et le NADPH est oxydé en NADP+ . La grande flexibilité de Met20 et d'autres boucles à proximité du site actif jouent un rôle dans la promotion de la libération du produit, le tétrahydrofolate. En particulier, la boucle Met20 aide à stabiliser le cycle nicotinamide du NADPH pour favoriser le transfert de l'hydrure du NADPH au dihydrofolate.
Le mécanisme de cette enzyme est aléatoire par étapes et à l'état d'équilibre. Plus précisément, la réaction catalytique commence avec la fixation du NADPH et du substrat au site de liaison de l'enzyme, suivie de la protonation et du transfert d'hydrure du cofacteur NADPH au substrat. Cependant, deux dernières étapes n'ont pas lieu simultanément dans un même état de transition. Dans une étude utilisant des approches informatiques et expérimentales, Liu et al concluent que l'étape de protonation précède le transfert d'hydrure.
Le mécanisme enzymatique de la DHFR s'avère être dépendant du pH, en particulier l'étape de transfert d'hydrure, car les changements de pH ont une influence remarquable sur l'électrostatique du site actif et l'état d'ionisation de ses résidus. L'acidité de l'azote ciblé sur le substrat est importante dans la liaison du substrat au site de liaison de l'enzyme qui s'avère hydrophobe même s'il est en contact direct avec l'eau. Asp27 est le seul résidu hydrophile chargé dans le site de liaison, et la neutralisation de la charge sur Asp27 peut altérer le pKa de l'enzyme. Asp27 joue un rôle critique dans le mécanisme catalytique en aidant à la protonation du substrat et en retenant le substrat dans la conformation favorable au transfert d'hydrure. L'étape de protonation est associée à la tautomérisation de l'énol même si cette conversion n'est pas considérée comme favorable pour le don de protons. Il est prouvé qu'une molécule d'eau est impliquée dans l'étape de protonation. L'entrée de la molécule d'eau sur le site actif de l'enzyme est facilitée par la boucle Met20.
Changements conformationnels de DHFR
Le cycle catalytique de la réaction catalysée par DHFR incorpore cinq intermédiaires importants : holoenzyme (E:NADPH), complexe de Michaelis (E:NADPH:DHF), complexe de produit ternaire (E:NADP + :THF), complexe binaire tétrahydrofolate (E:THF ), et le complexe THF‚NADPH (E:NADPH:THF). L'étape de dissociation du produit (THF) de E:NADPH:THF à E:NADPH est l'étape déterminant la vitesse pendant le renouvellement en régime permanent.
Les changements de conformation sont essentiels dans le mécanisme catalytique de DHFR. La boucle Met20 de DHFR est capable d'ouvrir, de fermer ou d'occlure le site actif. En conséquence, trois conformations différentes classées comme les états ouvert, fermé et occlus sont attribuées à Met20. De plus, une conformation déformée supplémentaire de Met20 a été définie en raison de ses résultats de caractérisation indistincts. La boucle Met20 est observée dans sa conformation occluse dans les trois produits intermédiaires de ligature, où le cycle nicotinamide est occlus du site actif. Cette caractéristique conformationnelle explique le fait que la substitution de NADP + par NADPH est antérieure à la dissociation du produit. Ainsi, le prochain cycle de réaction peut se produire lors de la liaison du substrat.
R67 DHFR
En raison de sa structure unique et de ses caractéristiques catalytiques, le R67 DHFR est largement étudié. R67 DHFR est une DHFR codée par un plasmide R de type II sans relation génétique et structurelle avec la DHFR chromosomique d'E. coli. C'est un homotétramère qui possède la symétrie 222 avec un seul pore de site actif qui est exposé au solvant [null .] Cette symétrie de site actif se traduit par le mode de liaison différent de l'enzyme : il peut se lier avec deux molécules de dihydrofolate (DHF) avec coopérativité positive ou deux molécules de NADPH à coopérativité négative, ou un substrat plus un, mais seule cette dernière a l'activité catalytique. Comparé à la DHFR chromosomique d'E. coli, elle a un K m plus élevé dans la liaison du dihydrofolate (DHF) et du NADPH. La cinétique catalytique beaucoup plus faible montre que le transfert d'hydrure est l'étape de détermination de la vitesse plutôt que la libération du produit (THF).
Dans la structure R67 DHFR, l'homotétramère forme un pore de site actif. Dans le processus catalytique, le DHF et le NADPH pénètrent dans le pore depuis une position opposée. L'interaction d'empilement π-π entre le cycle nicotinamide du NADPH et le cycle ptéridine du DHF relie étroitement deux réactifs dans le site actif. Cependant, la flexibilité de la queue p-aminobenzoylglutamate du DHF a été observée lors de la liaison, ce qui peut favoriser la formation de l'état de transition.
Signification clinique
Le déficit en dihydrofolate réductase a été lié à l'anémie mégaloblastique . Le traitement repose sur des formes réduites d'acide folique. Étant donné que le tétrahydrofolate, le produit de cette réaction, est la forme active du folate chez l'homme, l'inhibition de la DHFR peut provoquer une carence fonctionnelle en folate . La DHFR est une cible pharmaceutique attrayante pour l'inhibition en raison de son rôle central dans la synthèse des précurseurs d'ADN. Le triméthoprime , un antibiotique , inhibe la DHFR bactérienne tandis que le méthotrexate , un agent de chimiothérapie , inhibe la DHFR des mammifères. Cependant, une résistance s'est développée contre certains médicaments, à la suite de changements mutationnels dans la DHFR elle-même.
Les mutations DHFR provoquent une rare erreur innée autosomique récessive du métabolisme du folate qui entraîne une anémie mégaloblastique , une pancytopénie et une grave carence cérébrale en folate qui peut être corrigée par une supplémentation en acide folinique .
Applications thérapeutiques
Étant donné que le folate est nécessaire à la division rapide des cellules pour fabriquer la thymine , cet effet peut être utilisé à des fins thérapeutiques.
La DHFR peut être ciblée dans le traitement du cancer et comme cible potentielle contre les infections bactériennes. La DHFR est responsable des niveaux de tétrahydrofolate dans une cellule, et l'inhibition de la DHFR peut limiter la croissance et la prolifération des cellules caractéristiques du cancer et des infections bactériennes. Le méthotrexate , un inhibiteur compétitif de la DHFR, est l'un de ces médicaments anticancéreux qui inhibe la DHFR. D'autres médicaments comprennent le triméthoprime et la pyriméthamine . Ces trois sont largement utilisés comme agents antitumoraux et antimicrobiens. D'autres classes de composés ciblant la DHFR en général, et les DHFR bactériennes en particulier, appartiennent aux classes telles que les diaminoptéridines, les diaminotriazines, les diaminopyrroloquinazolines, les stilbènes, les chalcones, les désoxybenzoines, pour n'en citer que quelques-unes.
Le triméthoprime s'est révélé actif contre divers agents pathogènes bactériens à Gram positif . Cependant, la résistance au triméthoprime et à d'autres médicaments destinés à la DHFR peut survenir en raison d'une variété de mécanismes, limitant le succès de leurs utilisations thérapeutiques. La résistance peut provenir de l'amplification du gène DHFR, de mutations de la DHFR, d'une diminution de l'absorption des médicaments, entre autres. Quoi qu'il en soit, le triméthoprime et le sulfaméthoxazole en association sont utilisés comme agent antibactérien depuis des décennies.
Le folate est nécessaire à la croissance, et la voie du métabolisme du folate est une cible dans le développement de traitements contre le cancer. DHFR est l'une de ces cibles. Il a été démontré qu'un régime de fluorouracile , de doxorubicine et de méthotrexate prolonge la survie chez les patients atteints d'un cancer gastrique avancé. D'autres études sur les inhibiteurs de la DHFR peuvent conduire à d'autres moyens de traiter le cancer.
Les bactéries ont également besoin de DHFR pour croître et se multiplier et, par conséquent, des inhibiteurs sélectifs de la DHFR bactérienne ont trouvé une application en tant qu'agents antibactériens.
Les classes de petites molécules utilisées comme inhibiteurs de la dihydrofolate réductase comprennent la diaminoquinazoline et la diaminopyrroloquinazoline, la diaminopyrimidine, la diaminoptéridine et les diaminotriazines.
Traitement potentiel de l'anthrax
Dihydrofolate réductase de Bacillus anthracis (BaDHFR) une cible médicamenteuse validée dans le traitement de la maladie infectieuse, l'anthrax. Le BaDHFR est moins sensible aux analogues du triméthoprime que la dihydrofolate réductase d'autres espèces telles que Escherichia coli , Staphylococcus aureus et Streptococcus pneumoniae . Un alignement structurel de la dihydrofolate réductase des quatre espèces montre que seul le BaDHFR possède la combinaison phénylalanine et tyrosine aux positions 96 et 102, respectivement.
La résistance du BaDHFR aux analogues du triméthoprime est due à ces deux résidus (F96 et Y102), qui confèrent également une cinétique et une efficacité catalytique améliorées. La recherche actuelle utilise des mutants de site actif dans BaDHFR pour guider l'optimisation des pistes pour de nouveaux inhibiteurs d'antifolate.
En tant qu'outil de recherche
La DHFR a été utilisée comme outil pour détecter les interactions protéine-protéine dans un test de complémentation protéine-fragment (PCA).
Cellules CHO
Les cellules DHFR dépourvues de CHO sont la lignée cellulaire la plus couramment utilisée pour la production de protéines recombinantes. Ces cellules sont transfectées avec un plasmide portant le gène dhfr et le gène de la protéine recombinante dans un système d'expression unique , puis soumises à des conditions sélectives en milieu dépourvu de thymidine . Seules les cellules avec le gène DHFR exogène ainsi que le gène d'intérêt survivent.
Interactions
Il a été démontré que la dihydrofolate réductase interagit avec GroEL et Mdm2 .
Carte interactive des sentiers
Cliquez sur les gènes, les protéines et les métabolites ci-dessous pour accéder aux articles respectifs.
Les références
Lectures complémentaires
- Joska TM, Anderson AC (octobre 2006). "Relations structure-activité de Bacillus cereus et Bacillus anthracis dihydrofolate reductase: vers l'identification de nouvelles pistes médicamenteuses puissantes" . Agents antimicrobiens et chimiothérapie . 50 (10) : 3435-43. doi : 10.1128/AAC.00386-06 . PMC 1610094 . PMID 17005826 .
- Chan DC, Fu H, Forsch RA, Queener SF, Rosowsky A (juin 2005). « Conception, synthèse et activité antifolate de nouveaux analogues du piritrexim et d'autres inhibiteurs de la diaminopyrimidine dihydrofolate réductase avec substitution oméga-carboxyalcoxy ou oméga-carboxy-1-alcynyle dans la chaîne latérale ». Journal de chimie médicinale . 48 (13) : 4420-31. doi : 10.1021/jm0581718 . PMID 15974594 .
- Banerjee D, Mayer-Kuckuk P, Capiaux G, Budak-Alpdogan T, Gorlick R, Bertino JR (juillet 2002). « Nouveaux aspects de la résistance aux médicaments ciblant la dihydrofolate réductase et la thymidylate synthase » . Biochimica et Biophysica Acta (BBA) - Bases moléculaires de la maladie . 1587 (2-3): 164-73. doi : 10.1016/S0925-4439(02)00079-0 . PMID 12084458 .
- Stockman BJ, Nirmala NR, Wagner G, Delcamp TJ, DeYarman MT, Freisheim JH (janvier 1992). « Affectations de résonance 1H et 15N spécifiques à la séquence pour la dihydrofolate réductase humaine en solution ». Biochimie . 31 (1) : 218-29. doi : 10.1021/bi00116a031 . PMID 1731871 .
- Beltzer JP, Spiess M (décembre 1991). "Liaison in vitro du récepteur de l'asialoglycoprotéine à la bêta adaptine des vésicules recouvertes de membrane plasmique" . Le Journal de l'EMBO . 10 (12) : 3735-42. doi : 10.1002/j.1460-2075.1991.tb04942.x . PMC 453108 . PMID 1935897 .
- Davies JF, Delcamp TJ, Prendergast NJ, Ashford VA, Freisheim JH, Kraut J (octobre 1990). « Structures cristallines de la dihydrofolate réductase humaine recombinante complexée avec du folate et du 5-déazafolate ». Biochimie . 29 (40) : 9467-79. doi : 10.1021/bi00492a021 . PMID 2248959 .
- Will CL, Dolnick BJ (décembre 1989). "Le 5-fluorouracile inhibe le traitement de l'ARNm précurseur de la dihydrofolate réductase et/ou la stabilité de l'ARNm nucléaire dans les cellules KB résistantes au méthotrexate" . Le Journal de Chimie Biologique . 264 (35) : 21413-21. doi : 10.1016/S0021-9258 (19) 30096-1 . PMID 2592384 .
- Maîtres JN, Attardi G (mars 1985). "Transcrits discrets du gène de la dihydrofolate réductase humaine présents dans la carte d'ARN polysomal avec leurs extrémités 5' plusieurs centaines de nucléotides en amont du site de départ principal de l'ARNm" . Biologie moléculaire et cellulaire . 5 (3) : 493-500. doi : 10.1128/mcb.5.3.493 . PMC 366741 . PMID 2859520 .
- Miszta H, Dabrowski Z, Lanotte M (novembre 1988). « Modèles in vitro d'expression enzymatique de la tétrahydrofolate déshydrogénase (EC 1.5.1.3) dans les cellules stromales de la moelle osseuse ». Leucémie . 2 (11) : 754-9. PMID 3185016 .
- Oefner C, D'Arcy A, Winkler FK (juin 1988). « Structure cristalline de la dihydrofolate réductase humaine complexée avec du folate » . Journal Européen de Biochimie / FEBS . 174 (2) : 377–85. doi : 10.1111/j.1432-1033.1988.tb14108.x . PMID 3383852 .
- Yang JK, Masters JN, Attardi G (juin 1984). « Organisation du gène de la dihydrofolate réductase humaine. Conservation étendue de la séquence non codante 5' riche en G + C et forte divergence de la taille des introns par rapport aux gènes de mammifères homologues ». Journal de biologie moléculaire . 176 (2) : 169-87. doi : 10.1016/0022-2836(84)90419-4 . PMID 6235374 .
- Maîtres JN, Yang JK, Cellini A, Attardi G (juin 1983). « Un pseudogène humain dihydrofolate réductase et sa relation avec les multiples formes d'ARN messager spécifique ». Journal de biologie moléculaire . 167 (1) : 23-36. doi : 10.1016/S0022-2836(83)80032-1 . PMID 6306253 .
- Chen MJ, Shimada T, Moulton AD, Cline A, Humphries RK, Maizel J, Nienhuis AW (mars 1984). "Le gène fonctionnel de la dihydrofolate réductase humaine" . Le Journal de Chimie Biologique . 259 (6) : 3933-43. doi : 10.1016/S0021-9258 (17) 43186-3 . PMID 6323448 .
- Funanage VL, Myoda TT, Moses PA, Cowell HR (octobre 1984). "Affectation du gène de la dihydrofolate réductase humaine à la région q11----q22 du chromosome 5" . Biologie moléculaire et cellulaire . 4 (10) : 2010-6. doi : 10.1128/mcb.4.10.2010 . PMC 369017 . PMID 6504041 .
- Maîtres JN, Attardi G (1983). « La séquence nucléotidique de l'ADNc codant pour l'acide dihydrofolique réductase humaine ». Gène . 21 (1–2) : 59–63. doi : 10.1016/0378-1119(83)90147-6 . PMID 6687716 .
- Morandi C, Maîtres JN, Mottes M, Attardi G (avril 1982). "Plusieurs formes d'ARN messager de dihydrofolate réductase humaine. Clonage et expression dans Escherichia coli de leur séquence codante d'ADN". Journal de biologie moléculaire . 156 (3) : 583-607. doi : 10.1016/0022-2836(82)90268-6 . PMID 6750132 .
- Bonifaci N, Sitia R, Rubartelli A (septembre 1995). « La translocation nucléaire d'une protéine de fusion exogène contenant le VIH Tat nécessite un dépliage ». SIDA . 9 (9) : 995-1000. doi : 10.1097/00002030-199509000-00003 . PMID 8527095 . S2CID 8417864 .
- Mayhew M, da Silva AC, Martin J, Erdjument-Bromage H, Tempst P, Hartl FU (février 1996). « Repliement des protéines dans la cavité centrale du complexe de chaperonine GroEL-GroES ». Nature . 379 (6564) : 420-6. Bibcode : 1996Natur.379..420M . doi : 10.1038/379420a0 . PMID 8559246 . S2CID 4310511 .
- Gross M, Robinson CV, Mayhew M, Hartl FU, Radford SE (décembre 1996). "Une protection significative contre l'échange d'hydrogène dans le DHFR lié à GroEL est maintenue pendant les cycles itératifs de cyclage du substrat" . Sciences des protéines . 5 (12) : 2506–13. doi : 10.1002/pro.5560051213 . PMC 2143321 . PMID 8976559 .
- Schleiff E, Shore GC, Goping IS (mars 1997). "Récepteur d'importation mitochondrial humain, Tom20p. Utilisation du glutathion pour révéler des interactions spécifiques entre Tom20-glutathion S-transférase et les protéines précurseurs mitochondriales". Lettres FEBS . 404 (2-3): 314-8. doi : 10.1016/S0014-5793(97)00145-2 . PMID 9119086 . S2CID 29177508 .
- Cody V, Galitsky N, Luft JR, Pangborn W, Rosowsky A, Blakley RL (novembre 1997). « Comparaison de deux structures cristallines indépendantes de complexes ternaires de dihydrofolate réductase humaine réduits avec le phosphate de nicotinamide adénine dinucléotide et l'inhibiteur de liaison très étroit PT523 ». Biochimie . 36 (45) : 13897–903. doi : 10.1021/bi971711l . PMID 9374868 .
- Vanguri VK, Wang S, Godyna S, Ranganathan S, Liau G (avril 2000). "La thrombospondine-1 se lie à la polyhistidine avec une affinité et une spécificité élevées" . Le Journal Biochimique . 347 (Part 2) : 469–73. doi : 10.1042/0264-6021:3470469 . PMC 1220979 . PMID 10749676 .
Liens externes
- 1988 Conférence Nobel de médecine
- Proteopedia : Dihydrofolate réductase
- Aperçu de toutes les informations structurelles disponibles dans le PDB pour UniProt : P00374 (Dihydrofolate réductase) au PDBe-KB .