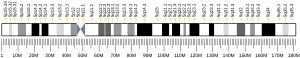MSH3 - MSH3
La protéine de réparation des mésappariements de l'ADN , MutS Homolog 3 (MSH3) est un homologue humain de la protéine bactérienne de réparation des mésappariements MutS qui participe au système de réparation des mésappariements (MMR). MSH3 forme typiquement l' hétérodimère MutSβ avec MSH2 afin de corriger les longues boucles d'insertion/délétion et les mésappariements base-base dans les microsatellites pendant la synthèse d'ADN. Une capacité déficiente pour le ROR se retrouve dans environ 15 % des cancers colorectaux , et des mutations somatiques du gène MSH3 peuvent être trouvées dans près de 50 % des cancers colorectaux déficients en ROR.
Gène et expression
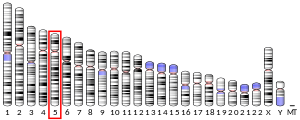
Chez l'homme, le gène codant pour MSH3 se trouve sur le chromosome 5 à l'emplacement 5q11-q12 en amont du gène de la dihydrofolate réductase (DHFR). MSH3 est codé par 222 341 paires de bases et crée une protéine constituée de 1137 acides aminés.
Le MSH3 est généralement exprimé à de faibles niveaux dans plusieurs lignées cellulaires transformées, notamment HeLa , K562 , HL-60 et CEM, ainsi que dans une large gamme de tissus normaux, notamment la rate, le thymus, la prostate, les testicules, l'ovaire, l'intestin grêle, le côlon, leucocytes du sang périphérique, cœur, cerveau, placenta, poumon, foie, muscle squelettique, rein et pancréas. Bien que les niveaux d'expression de MSH3 varient légèrement d'un tissu à l'autre, son faible niveau d'expression répandu indique qu'il s'agit d'un gène « d'entretien » couramment exprimé dans toutes les cellules.
La surexpression de MSH3 a diminué la capacité de MMR. Lorsque MSH3 est surexprimé, des changements drastiques se produisent dans les niveaux relatifs de formation de MutSβ aux dépens de MutSα. MutSα est responsable des mésappariements base-base et des boucles d'insertion/délétion courtes, tandis que MutSβ répare les boucles d'insertion/délétion longues dans l'ADN. Un changement drastique des niveaux relatifs de ces complexes protéiques peut entraîner une diminution de la capacité de MMR. Dans le cas de la surexpression de MSH3, MSH2 s'hétérodimérise préférentiellement avec MSH3 conduisant à des niveaux élevés de MutSβ et à la dégradation de la protéine MSH6 sans partenaire qui se complexe normalement avec MSH2 pour former MutSα.
Interactions
Il a été démontré que MSH3 interagit avec MSH2, PCNA et BRCA1 . Ces interactions forment des complexes protéiques qui sont généralement impliqués dans les activités de suppression tumorale et de réparation de l'ADN.
L'interaction principale de MSH3 implique la formation du complexe MutSβ avec MSH2. MutSβ se forme comme un hétérodimère de MSH2 et MSH3 avec deux régions d'interaction primaires : une région amino-terminale et une région carboxy-terminale . La région N-terminale de MSH3 (acides aminés 126-250) est en contact avec la région N-terminale de MSH2 aa 378-625. Les régions C-terminales se connectent à aa 1050-1128 de MSH3 et aa 875-934 de MSH2. Les régions de liaison sur MSH2 sont identiques lors de la liaison à MSH3 ou MSH6. Les régions de liaison aux nucléotides d' adénine dans MSH3 et MSH2 ne sont contenues dans aucune des régions d'interaction impliquées dans la dimérisation, permettant à MutSβ de se lier à l'ADN et d'effectuer la MMR.
| Image externe | |
|---|---|
|
|
L'antigène nucléaire de prolifération cellulaire (PCNA) est une protéine impliquée dans le ROR post-réplication. Il a été montré que PCNA se lie à l'hétérodimère MutSβ via un motif de liaison dans le domaine N-terminal de MSH3. Le PCNA lié localise ensuite le complexe MutSβ aux foyers de réplication, indiquant que le PCNA aide à initier la réparation en guidant MutSβ et d'autres protéines de réparation vers des extrémités libres dans l'ADN récemment répliqué.
Fonction
La fonction principale de MSH3 est de maintenir la stabilité du génome et de décréter la suppression tumorale en formant l'hétérodimère MutSβ pour corriger les longues boucles d'insertion/délétion et les mésappariements base-base. Dans le cas de longues boucles d'insertion/suppression, l'ADN est fortement courbé et les paires de bases en aval peuvent devenir non appariées et exposées. MutSβ reconnaît les boucles d'insertion/suppression de 1 à 15 nucléotides ; la liaison aux boucles d'insertion/suppression est obtenue en insérant le domaine de liaison de mésappariement de MSH3 et une partie du domaine de liaison de mésappariement de MSH2 dans le sillon formé par la courbure extrême de l'ADN formée par la boucle d'insertion/suppression.
| Image externe | |
|---|---|
|
|
Rôle dans le cancer
Le rôle le plus important de MSH3 dans le cancer est la suppression des tumeurs par la réparation des mutations somatiques dans l'ADN qui se produisent à la suite de désappariements base-base et de boucles d'insertion/délétion. La perte d'expression et la surexpression de MSH3 peuvent entraîner des effets cancérigènes .
La surexpression de MSH3 peut entraîner des changements drastiques dans les niveaux relatifs d'e de MutSα et MutSβ. Normalement, MutSβ est exprimé à des niveaux relativement faibles dans toutes les cellules tandis que MutSα est présent à des niveaux élevés. Alors que les deux protéines ont une fonction redondante dans les réparations base-base, MutSα effectue généralement des réparations de mésappariement base-base et effectue également des réparations sur les boucles d'inertie/délétion courtes les plus courantes. Lorsque MSH3 est fortement surexprimé, il agit comme un séquestre pour MSH2 et les niveaux relatifs de MutSβ et MutSα changent considérablement à mesure que les protéines MSH6 non appariées se dégradent et que MutSα s'épuise. MutSβ peut compenser quelque peu la perte des fonctions de correction de désappariement base-base, mais n'est pas adapté à la réparation de nombreuses boucles d'insertion/suppression courtes de 1 à 2 paires de bases. Cela conduit à un taux accru d'instabilités microsatellites et à des taux accrus de mutations somatiques.
Cet effet est directement lié au cancer humain sous forme de résistance aux médicaments. L' amplification du gène DHFR est l'une des réponses de résistance courantes au méthotrexate , un médicament couramment utilisé pour traiter la leucémie lymphoïde aiguë chez l' enfant et diverses autres tumeurs . L'amplification de la DHFR conduit à une surexpression de MSH3 et a été liée à une récidive pharmacorésistante dans le cancer.
En revanche, la perte de MSH3 peut entraîner un déficit de réparation des mésappariements et une instabilité génétique qui ont été identifiés comme des effets cancérigènes particulièrement courants dans le cancer colorectal humain. Les mutations provoquant le knockdown de MSH3 peuvent entraîner une diminution de la capacité des cellules à réparer de longues boucles d'insertion/délétion provoquant des instabilités microsatellites (MSI) dans le génome et permettant une augmentation des taux de mutation somatique. Les altérations microsatellites élevées au niveau des répétitions tétranucléotidiques sélectionnées (EMAST) sont un type de MSI où les loci contenant des répétitions tétranucléotidiques AAAG ou ATAG sont particulièrement instables. Les phénotypes EMAST sont particulièrement fréquents, avec près de 60% des cancers colorectaux sporadiques présentant des niveaux élevés d'EMAST liés à un taux élevé de cellules déficientes en MSH3 dans les tumeurs.
Les références
Lectures complémentaires
- Marti TM, Kunz C, Fleck O (2002). « Voies de réparation des mésappariements de l'ADN et d'évitement des mutations » . J. Cell. Physiol . 191 (1) : 28-41. doi : 10.1002/jcp.10077 . PMID 11920679 . S2CID 35468455 .
- Fujii H, Shimada T (1989). "Isolement et caractérisation des clones d'ADNc dérivés du gène transcrit de manière divergente dans la région en amont du gène de la dihydrofolate réductase humaine" . J. Biol. Chem . 264 (17) : 10057-64. doi : 10.1016/S0021-9258 (18) 81766-5 . PMID 2722860 .
- Chen MJ, Shimada T, Moulton AD, et al. (1984). "Le gène fonctionnel de la dihydrofolate réductase humaine" . J. Biol. Chem . 259 (6) : 3933-43. doi : 10.1016/S0021-9258 (17) 43186-3 . PMID 6323448 .
- Shinya E, Shimada T (1994). "Identification de deux éléments initiateurs dans le promoteur bidirectionnel des gènes de la dihydrofolate réductase humaine et de la protéine de réparation des mésappariements 1" . Acides nucléiques Res . 22 (11) : 2143-9. doi : 10.1093/nar/22.11.2143 . PMC 308133 . PMID 8029024 .
- Risinger JI, Umar A, Boyd J, et al. (1996). « Mutation de MSH3 dans le cancer de l'endomètre et preuve de son rôle fonctionnel dans la réparation hétéroduplex ». Nat. Genet . 14 (1) : 102-5. doi : 10.1038/ng0996-102 . PMID 8782829 . S2CID 25456490 .
- Watanabe A, Ikejima M, Suzuki N, Shimada T (1997). « Organisation génomique et expression du gène MSH3 humain ». Génomique . 31 (3) : 311-8. doi : 10.1006/geno.1996.0053 . PMID 8838312 .
- Nakajima E, Orimo H, Ikejima M, Shimada T (1996). « Polymorphisme de répétition de neuf pb dans l'exon 1 du gène hMSH3 » . Japon. J. Hum. Genet . 40 (4) : 343-5. doi : 10.1007/BF01900603 . PMID 8851770 .
- Acharya S, Wilson T, Gradia S, et al. (1997). "hMSH2 forme des complexes de liaison de mésappariement spécifiques avec hMSH3 et hMSH6" . Proc. Natl. Acad. Sci. États-Unis . 93 (24) : 13629-34. doi : 10.1073/pnas.93.24.13629 . PMC 19374 . PMID 8942985 .
- Guerrette S, Wilson T, Gradia S, Fishel R (1998). « Interactions de hMSH2 humain avec hMSH3 et hMSH2 avec hMSH6 : examen des mutations trouvées dans le cancer colorectal héréditaire sans polypose » . Mol. Cellule. Biol . 18 (11) : 6616-23. doi : 10.1128/mcb.18.11.6616 . PMC 109246 . PMID 9774676 .
- Ceccotti S, Ciotta C, Fronza G, et al. (2000). "De multiples mutations et décalages de cadre sont la marque de hPMS2 défectueux dans les cellules tumorales humaines transfectées par pZ189" . Acides nucléiques Res . 28 (13) : 2577–84. doi : 10.1093/nar/28.13.2577 . PMC 102707 . PMID 10871409 .
- Orimo H, Nakajima E, Yamamoto M, et al. (2000). "Association entre les polymorphismes nucléotidiques simples du gène hMSH3 et le cancer du côlon sporadique avec instabilité des microsatellites" . J. Hum. Genet . 45 (4) : 228-30. doi : 10.1007/s100380070031 . PMID 10944853 .
- Clark AB, Valle F, Drotschmann K, et al. (2001). "Interaction fonctionnelle de l'antigène nucléaire cellulaire proliférant avec les complexes MSH2-MSH6 et MSH2-MSH3" . J. Biol. Chem . 275 (47) : 36498–501. doi : 10.1074/jbc.C000513200 . PMID 11005803 .
- Kleczkowska HE, Marra G, Lettieri T, Jiricny J (2001). "hMSH3 et hMSH6 interagissent avec PCNA et colocalisent avec lui aux foyers de réplication" . Gènes Dev . 15 (6) : 724–36. doi : 10.1101/gad.191201 . PMC 312660 . PMID 11274057 .
- Schmutte C, Sadoff MM, Shim KS et al. (2001). "L'interaction des protéines de réparation des mésappariements d'ADN avec l'exonucléase I humaine." J. Biol. Chem . 276 (35) : 33011-8. doi : 10.1074/jbc.M102670200 . PMID 11427529 .
- Wang Q, Zhang H, Guerrette S et al. (2001). "Le nucléotide d'adénosine module l'interaction physique entre hMSH2 et BRCA1" . Oncogène . 20 (34): 4640-9. doi : 10.1038/sj.onc.1204625 . PMID 11498787 .
- Mazurek A, Berardini M, Fishel R (2002). "Activation d'homologues MutS humains par des dommages à l'ADN 8-oxo-guanine" . J. Biol. Chem . 277 (10) : 8260-6. doi : 10.1074/jbc.M111269200 . PMID 11756455 .
- Plotz G, Raedle J, Brieger A, et al. (2002). "hMutSalpha forme un complexe ATP-dépendant avec hMutLalpha et hMutLbeta sur l'ADN" . Acides nucléiques Res . 30 (3) : 711-8. doi : 10.1093/nar/30.3.711 . PMC 100294 . PMID 11809883 .
- Arzimanoglou II, Hansen LL, Chong D, et al. (2002). « LOH fréquent à hMLH1, un SNP très variable dans hMSH3 et une instabilité de codage négligeable dans le cancer de l'ovaire ». Rés anticancéreux . 22 (2A) : 969–75. PMID 12014680 .
- Ohta S, Shiomi Y, Sugimoto K, et al. (2002). "Une approche protéomique pour identifier les protéines de liaison à l'antigène nucléaire cellulaire proliférant (PCNA) dans les lysats de cellules humaines. Identification du complexe humain CHL12/RFCs2-5 en tant que nouvelle protéine de liaison au PCNA" . J. Biol. Chem . 277 (43): 40362-7. doi : 10.1074/jbc.M206194200 . PMID 12171929 .